聚类算法之PCA与tSNE
Posted 单细胞天地
tags:
篇首语:本文由小常识网(cha138.com)小编为大家整理,主要介绍了聚类算法之PCA与tSNE相关的知识,希望对你有一定的参考价值。

课程笔记
粉丝:有单细胞线上课程吗?
小编:什么 ? 我们的单细胞转录组分析线上课程已经上线好久了,你们竟然都不知道吗,每篇推文后面的课程推荐没人看的吗,小编已哭晕在厕所
? 我们的单细胞转录组分析线上课程已经上线好久了,你们竟然都不知道吗,每篇推文后面的课程推荐没人看的吗,小编已哭晕在厕所
好了,戏演完了,下面郑重介绍下我们的单细胞线上课程:(详情戳下方链接)
这个课程笔记栏目记录了学员们学习单细胞转录组课程的学习笔记
希望大家能有所收获!

前 · 言
第二单元第六讲:聚类算法之PCA与tSNE
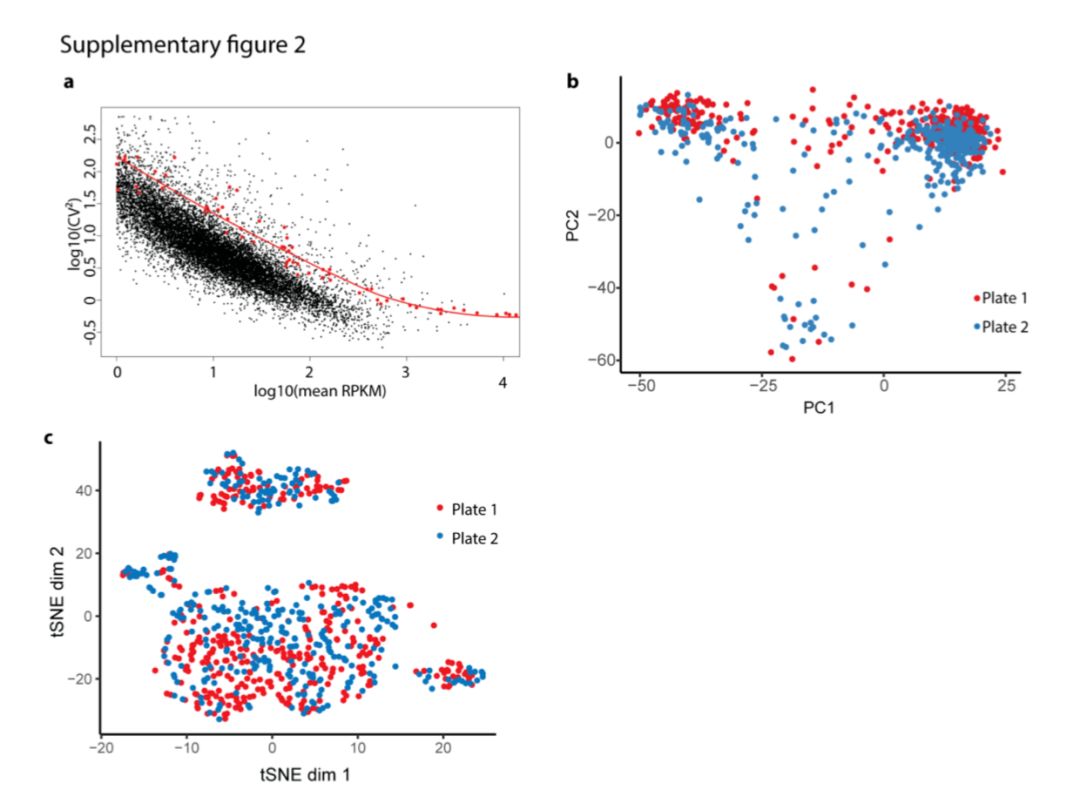
还是之前文章附件的图片,其中b图是选取两个主成分做的PCA图,c图是tSNE图:
几个常用函数的转置t(transpose),傻傻分不清?: 计算距离介绍过
dist()函数,它是按行为操作对象,而聚类是要对样本聚类,因此要先将我们平时见到的表达矩阵(行为基因,列为样本)转置;同样PCA也是对行/样本进行操作,也是需要先转置;另外归一化的scale()函数虽然是对列进行操作,但它的对象是基因,因此也需要转置
关于PCA的学习,之前写过:
StatQuest-PCA学习:https://www.jianshu.com/p/b83ac8f7f5a7
StatQuest--在R中拆解PCA:https://www.jianshu.com/p/8a74508c3737
先构建一个非常随机的测试数据
# 设置随机种子,可以重复别人使用的随机数
set.seed(123456789)
library(pheatmap)
library(Rtsne)
library(ggfortify)
library(mvtnorm)
# 设置两个正态分布的随机矩阵(500*20)
ng=500
nc=20
a1=rnorm(ng*nc);dim(a1)=c(ng,nc)
a2=rnorm(ng*nc);dim(a2)=c(ng,nc)
a3=cbind(a1,a2)
> dim(a3)
[1] 500 40
# 添加列名
colnames(a3)=c(paste0('cell_01_',1:nc),
paste0('cell_02_',1:nc))
# 添加行名
rownames(a3)=paste('gene_',1:ng,sep = '')
# 先做个热图
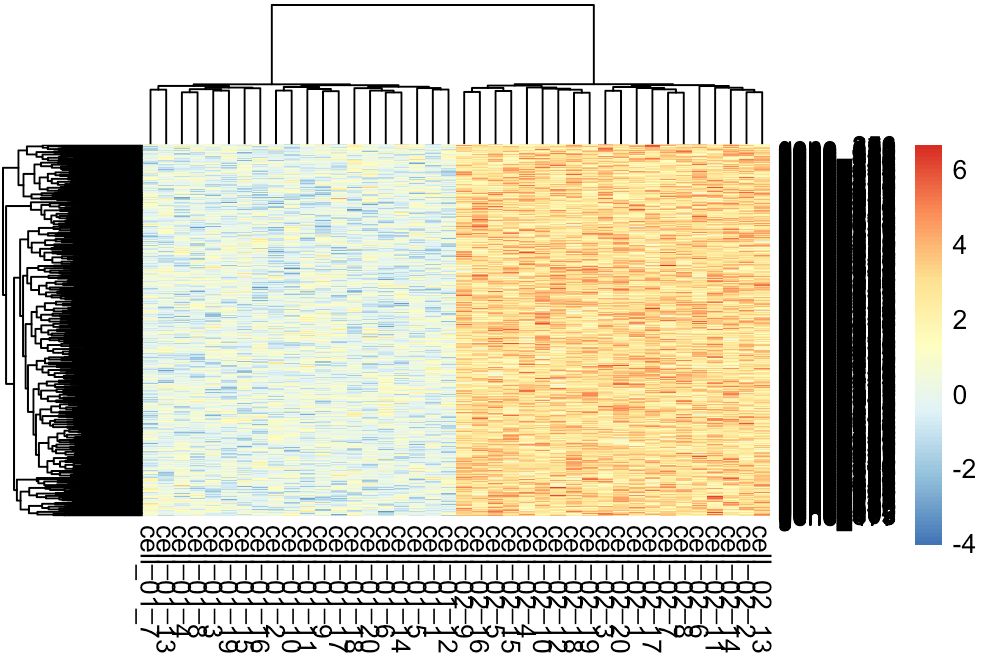
pheatmap(a3)
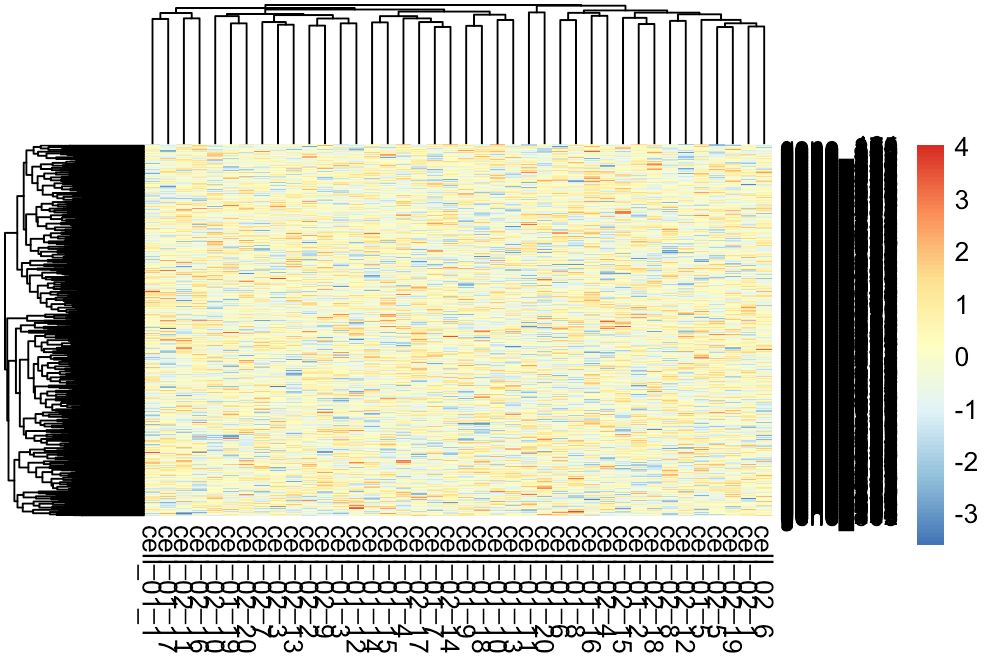
没有体现任何的基因差异或者样本聚类(热图中的聚类是自然层次聚类),可以看到样本名都是无规律的交叉显示
如果做PCA呢?
# 先转置一下,让行为样本
> a3=t(a3);dim(a3)
[1] 40 500
# prcomp()主成分分析
pca_dat <- prcomp(a3, scale. = TRUE)
p=autoplot(pca_dat) + theme_classic() + ggtitle('PCA plot')
print(p)
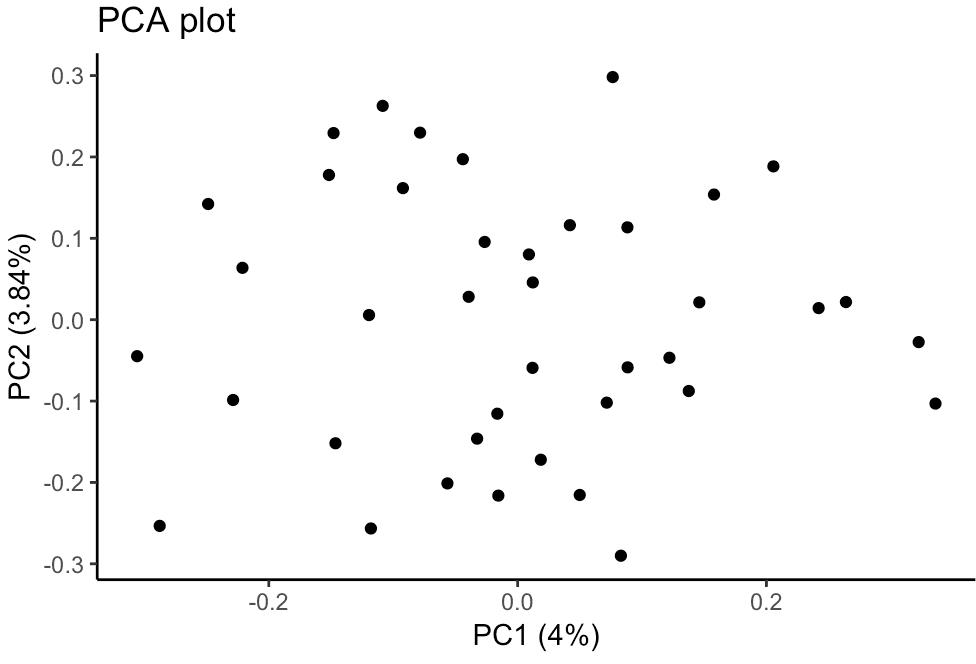
可以看到每组的20个细胞都分不开,但每组具体有哪些样本还是看不出来,因此这里为每组加上颜色来表示
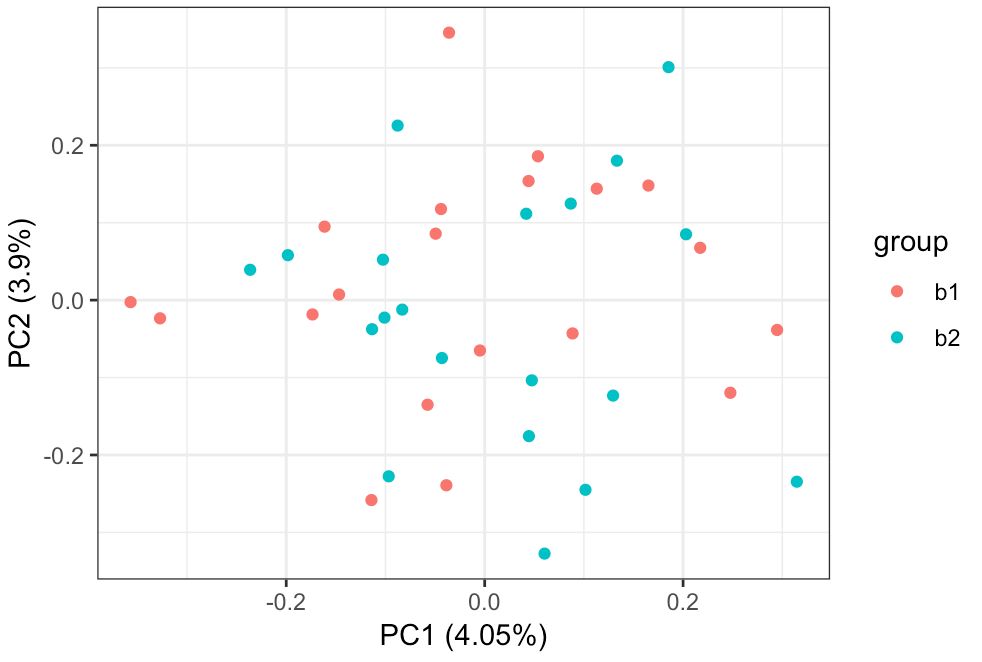
# 先在原来数据的基础上添加样本分组信息(别忘了a3是一个矩阵,先转换成数据框)
df=cbind(as.data.frame(a3),group=c(rep('b1',20),rep('b2',20)))
autoplot(prcomp( df[,1:(ncol(df)-1)] ), data=df,colour = 'group')+theme_bw()
另外看下tsne
利用了一个核心函数Rtsne()
set.seed(42)
tsne_out <- Rtsne(a3,pca=FALSE,perplexity=10,theta=0.0)
# 结果得到一个列表
> str(tsne_out)
List of 14
$ N : int 40
$ Y : num [1:40, 1:2] -36.7 -28 -168 -33.4 22.4 ...
$ costs : num [1:40] 0.00348 -0.00252 0.01496 0.01646 0.00951 ...
# 其中在Y中存储了画图坐标
> head(tsne_out$Y,3)
[,1] [,2]
[1,] -36.72621 -78.03709
[2,] -28.00151 33.30229
[3,] -167.98560 -80.26850
tsnes=tsne_out$Y
colnames(tsnes) <- c("tSNE1", "tSNE2") #为坐标添加列名
# 基础作图代码
ggplot(tsnes, aes(x = tSNE1, y = tSNE2))+ geom_point()
# 在此基础上添加颜色分组信息,首先还是将tsnes这个矩阵变成数据框,然后增加一列group信息,最后映射在geom_point中
tsnes=as.data.frame(tsnes)
group=c(rep('b1',20),rep('b2',20))
tsnes$group=group
ggplot(tsnes, aes(x = tSNE1, y = tSNE2))+ geom_point(aes(col=group))
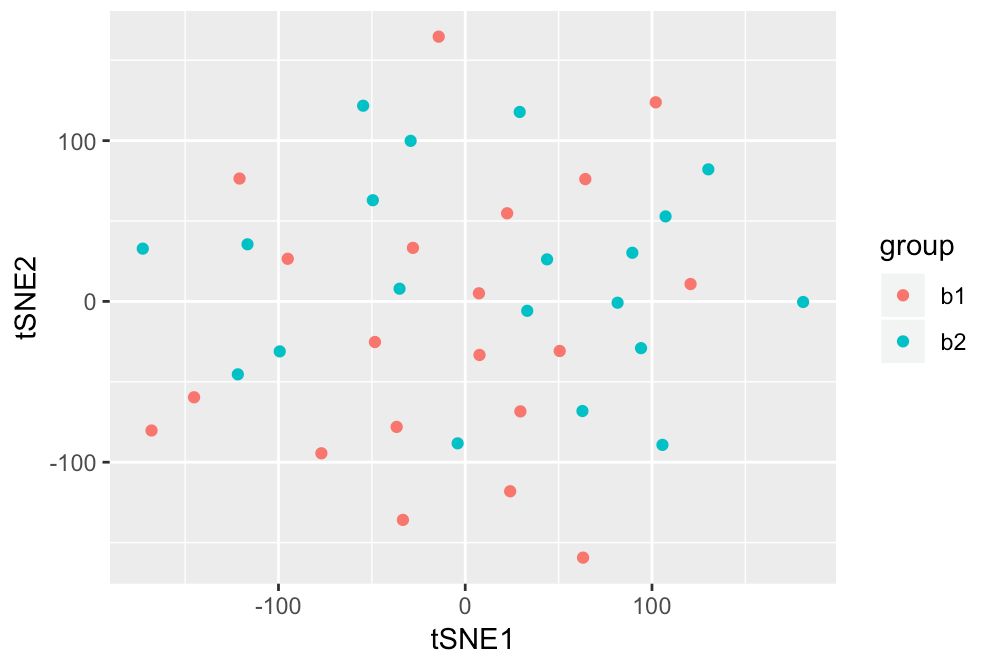
构建一个有规律的测试数据
ng=500
nc=20
a1=rnorm(ng*nc);dim(a1)=c(ng,nc)
# 和之前的区别就在a2这里,都加了3
a2=rnorm(ng*nc)+3;dim(a2)=c(ng,nc)
a3=cbind(a1,a2)
colnames(a3)=c(paste0('cell_01_',1:nc),paste0('cell_02_',1:nc))
rownames(a3)=paste('gene_',1:ng,sep = '')
pheatmap(a3)
热图已经能看出来差异了,再看看PCA
a3=t(a3);dim(a3)
df=cbind(as.data.frame(a3),group=c(rep('b1',20),rep('b2',20)))
autoplot(prcomp( df[,1:(ncol(df)-1)] ), data=df,colour = 'group')+theme_bw()
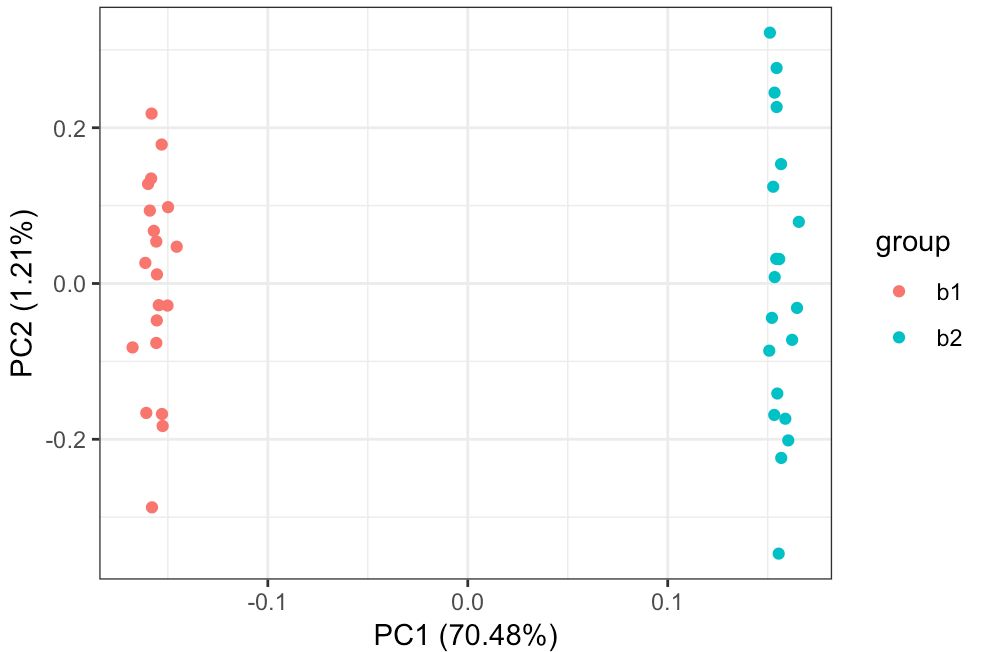
tsne也是如此
set.seed(42)
tsne_out <- Rtsne(a3,pca=FALSE,perplexity=10,theta=0.0)
tsnes=tsne_out$Y
colnames(tsnes) <- c("tSNE1", "tSNE2")
tsnes=as.data.frame(tsnes)
group=c(rep('b1',20),rep('b2',20))
tsnes$group=group
ggplot(tsnes, aes(x = tSNE1, y = tSNE2))+ geom_point(aes(col=group))
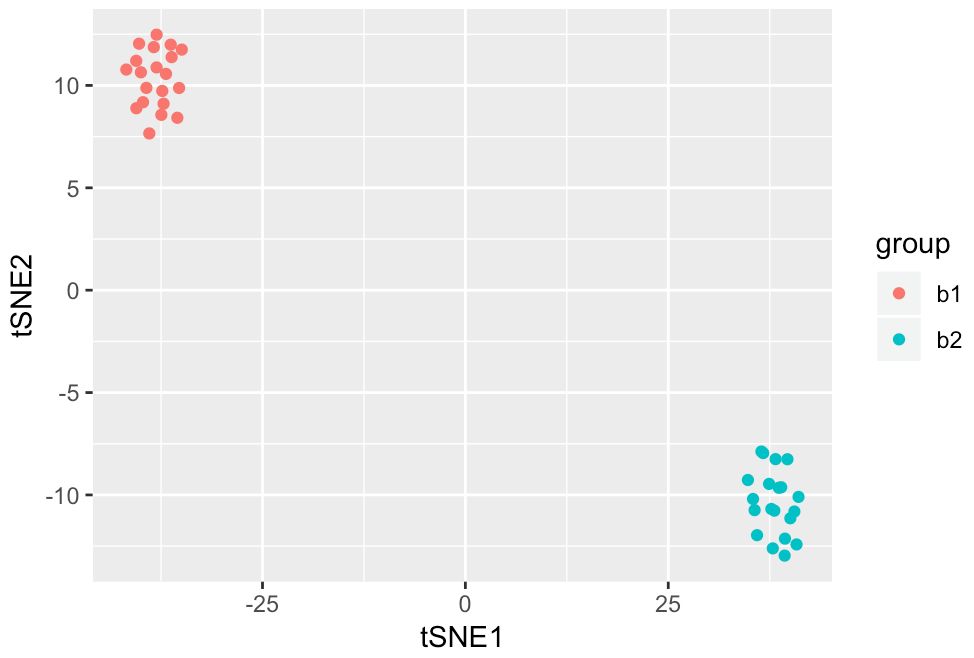
真实数据演练
载入RPKM数据
rm(list = ls())
options(stringsAsFactors = F)
load(file = '../input_rpkm.Rdata')
# 表达量信息
> dat[1:2,1:3]
SS2_15_0048_A3 SS2_15_0048_A6 SS2_15_0048_A5
0610007P14Rik 0 0 74.95064
0610009B22Rik 0 0 0.00000
# 样本属性
> head(metadata,3)
g plate n_g all
SS2_15_0048_A3 1 0048 3065 all
SS2_15_0048_A6 2 0048 3036 all
SS2_15_0048_A5 1 0048 3742 all
#所有数据的聚类分组信息
group_list=metadata$g
#批次信息
plate=metadata$plate
> table(plate)
plate
0048 0049
384 384
对数据进行PCA
# 操作前先备份
dat_back=dat
# 先对表达矩阵进行转置,然后转换成数据框,就可以添加批次信息了
dat=dat_back
dat=t(dat)
dat=as.data.frame(dat)
dat=cbind(dat,plate )
> dim(dat_back)
[1] 12689 768
> dim(dat)
[1] 768 12690
library("FactoMineR")
library("factoextra")
dat.pca <- PCA(dat[,-ncol(dat)], graph = FALSE)
fviz_pca_ind(dat.pca, # repel =T,
geom.ind = "point", # 只显示点,不显示文字
col.ind = dat$plate, # 按分组上色
#palette = c("#00AFBB", "#E7B800"),
addEllipses = TRUE, # 添加晕环
legend.title = "Groups"
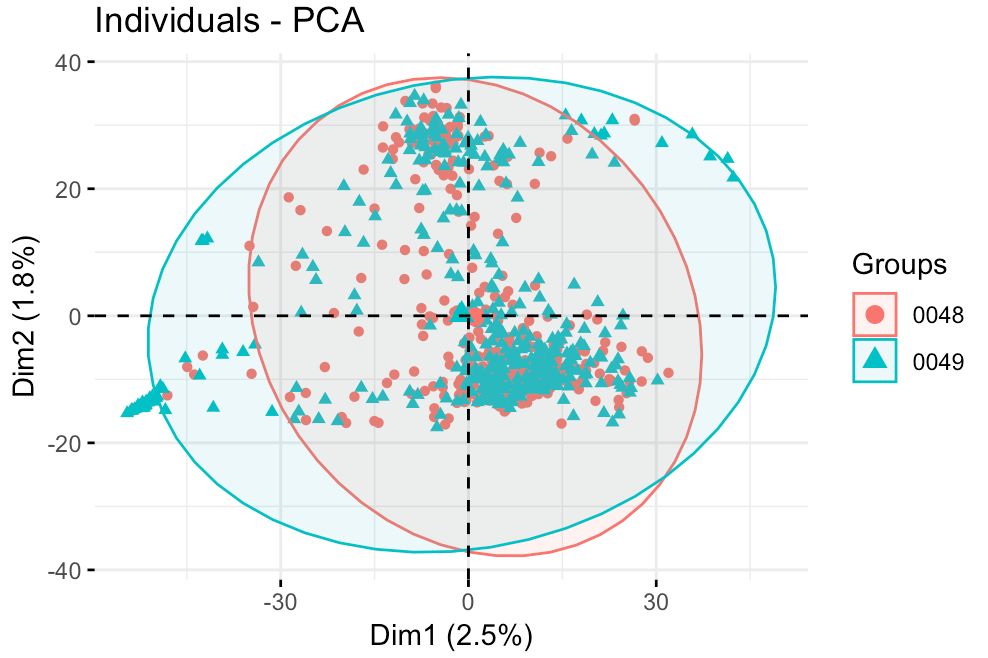
可以看到两个批次之间分不开,说明没有批次效应
如果你对单细胞转录组研究感兴趣,但又不知道如何入门,也许你可以关注一下下面的课程
以上是关于聚类算法之PCA与tSNE的主要内容,如果未能解决你的问题,请参考以下文章
PCA图像数据降维及重构误差分析实战并使用TSNE进行异常数据可视化分析